Simulan por primera vez una célula viva completa en un ordenador
Un equipo internacional de científicos ha recreado por primera vez en un ordenador el ciclo completo de una célula viva, desde la replicación del ADN hasta su división. La simulación, que sigue el comportamiento de cada molécula en cuatro dimensiones, abre una nueva forma de estudiar los procesos fundamentales de la vida.
Por Enrique Coperías, periodista científico
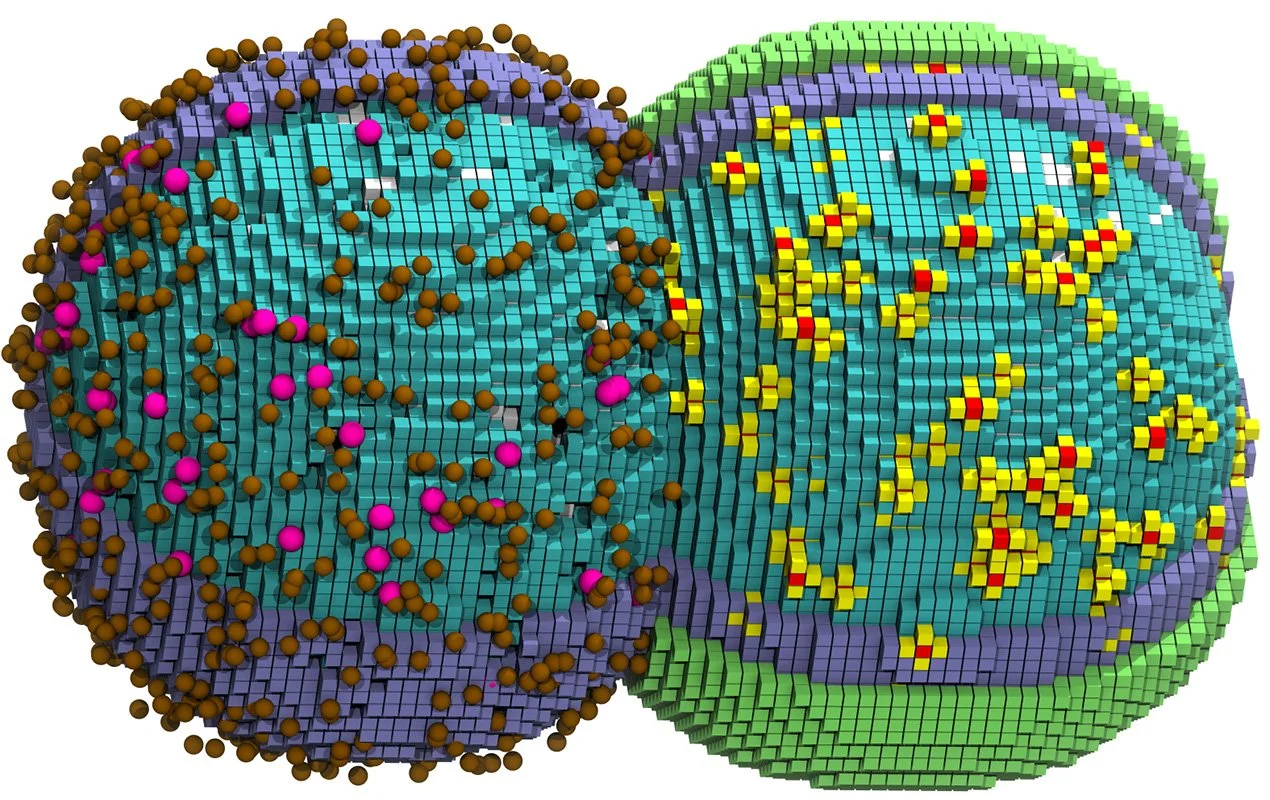
Simulación de una célula en las primeras fases de la división: la mitad izquierda muestra el citoplasma (cubos azules), las moléculas responsables de la degradación del ARN mensajero (rosa) y los transportadores de azúcares (marrón); la mitad derecha añade la membrana celular (verde) y los ribosomas (amarillo/rojo). Cortesía: Cell / DOI: 10.1016/j.cell.2026.02.009
Una célula viva dentro de un ordenador
Un equipo internacional de investigadores ha dado un paso que hace apenas unas décadas parecía propio de la ciencia ficción: recrear el ciclo completo de una célula viva dentro de un ordenador. El trabajo, publicado en la revista Cell, describe la primera simulación que reproduce en cuatro dimensiones —tres espaciales más el tiempo— todo el proceso por el que una célula crece, replica su ADN y se divide en dos.
El logro no consiste simplemente en visualizar una célula. El modelo integra miles de reacciones químicas, procesos genéticos y transformaciones físicas para seguir, segundo a segundo, cómo se desarrolla la vida en su forma más simple. En palabras de sus autores, la simulación permite observar cómo «los procesos químicos y físicos subyacentes impulsan la progresión del estado celular a lo largo del tiempo».
La investigación representa uno de los intentos más ambiciosos de la biología computacional: construir una célula virtual capaz de reproducir el comportamiento de una célula real. Si ese objetivo se alcanza plenamente, podría transformar la forma de estudiar la vida, y permitir de paso la experimentación en el ordenador con organismos completos antes de hacerlo en el laboratorio.
La célula más simple posible
El modelo se basa en un organismo singular: JCVI-syn3A, una bacteria con un genoma mínimo diseñado por el Instituto J. Craig Venter, en Estados Uniudos. Este microorganismo contiene solo 493 genes y un cromosoma circular de unas 543.000 bases o letras genéticas, lo que lo convierte en uno de los sistemas vivos más simples capaces de crecer y dividirse por sí mismos. Los laboratorios de los coautores del estudio, Angad Mehta, profesor de Química en la Universidad de Illinois, y Taekjip Ha, del Hospital Infantil de Boston y la Facultad de Medicina de Harvard, generaron datos experimentales adicionales que permitieron al equipo simular y validar con precisión numerosos aspectos de la función celular.
Precisamente la simplicidad de JCVI-syn3A lo convierte en el candidato ideal para intentar algo extraordinariamente complejo: simular todos los procesos que ocurren dentro de una célula.
🗣️ «Este es un modelo cinético tridimensional y totalmente dinámico de una célula mínima viva que imita lo que ocurre en la célula real. Un proyecto tan ambicioso solo fue posible gracias al esfuerzo combinado de numerosos colaboradores de la Universidad de Illinois y de la Facultad de Medicina de Harvard, donde modelamos sistemáticamente el metabolismo esencial y otras redes subcelulares a través de una serie de publicaciones que comenzaron en 2018», explica Zan Luthey-Schulten, química de la Universidad de Illinois Urbana-Champaign y líder del estudio.
En la simulación, los investigadores reprodujeron un ciclo celular completo de unos cien minutos, el tiempo que tarda esta bacteria en duplicarse en condiciones normales. Durante ese periodo, el modelo sigue simultáneamente:
1️⃣ La expresión de todos sus genes.
2️⃣ Las reacciones metabólicas que producen energía y moléculas básicas.
3️⃣ La replicación del ADN.
4️⃣ La síntesis de proteínas en los ribosomas.
5️⃣ El crecimiento de la membrana.
6️⃣ La división celular.
Cada molécula relevante —proteínas, ARN o complejos celulares— se representa como una partícula individual que puede moverse, reaccionar o interactuar con otras dentro del espacio tridimensional de la célula.
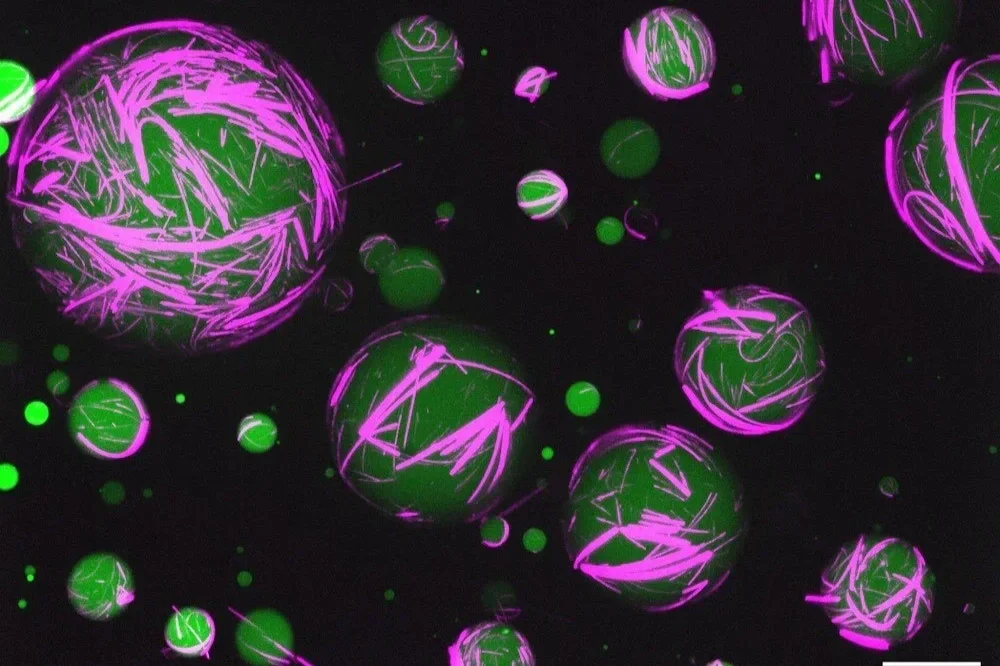
Modelos generados por ordenador de la célula mínima sintética JCVI-syn3A. Cortesía: University of Illinois at Urbana-Champaign.
Una célula en cuatro dimensiones
Hasta ahora, muchos modelos celulares trataban el interior de la célula como si fuese un líquido perfectamente mezclado. Eso simplifica los cálculos, pero no refleja la realidad. En una célula verdadera, las moléculas se desplazan lentamente, chocan entre sí y reaccionan solo cuando se encuentran.
El nuevo modelo intenta capturar ese comportamiento realista. Para ello divide el interior celular en una cuadrícula tridimensional con cubos de apenas 10 nanómetros, donde ocurren las reacciones químicas y los movimientos de difusión molecular.
Además, el ADN se modela como un polímero flexible compuesto por unidades que representan fragmentos de diez pares de bases. Este cromosoma virtual puede doblarse, formar bucles o separarse durante la replicación, imitando el comportamiento físico del ADN real.
El resultado es una simulación en cuatro dimensiones: no solo muestra la estructura de la célula, sino también cómo cambia con el tiempo.
Crecer, copiarse y dividirse
Uno de los mayores desafíos fue reproducir los procesos que permiten a la célula multiplicarse. En la simulación, el crecimiento ocurre cuando se incorporan nuevos lípidos y proteínas a la membrana celular, aumentando así su superficie. Al mismo tiempo, el ADN se duplica siguiendo el conocido mecanismo de replicación, mientras las proteínas responsables de la división celular preparan la separación final.
El modelo logra reproducir con notable precisión el comportamiento observado en el laboratorio. Por ejemplo, predice un tiempo de duplicación de unos 105 minutos, prácticamente idéntico al medido experimentalmente para esta bacteria.
También reproduce la proporción entre el origen y el final del cromosoma durante la replicación, un indicador utilizado por los biólogos para evaluar la dinámica del ADN en poblaciones celulares.
Incluso puede reflejar cómo cada célula es ligeramente diferente. Debido al carácter aleatorio de las reacciones moleculares, cada simulación produce una trayectoria distinta: algunas células inician la replicación del ADN antes, otras un poco más tarde. Esa variabilidad también se observa en organismos reales.
🗣️ «En simulaciones repetidas con células individuales que partían de condiciones iniciales ligeramente diferentes, el ciclo celular simulado se producía, de media, con una diferencia de solo dos minutos respecto al ciclo celular real», explica Zane Thornburg, uno de los investigadores que desarrolló el modelo.
Además, los datos experimentales incorporados al estudio ayudaron a confirmar características fundamentales del organismo simulado. “Lo más importante es que su trabajo reveló el alcance de la replicación del ADN y que la división celular de Syn3A es simétrica”, señala Luthey-Schulten.
UNA CÉLULA VIRTUAL EN ACCIÓN
Simulación del ciclo celular de una célula virtual, que incluye los cromosomas modelados mediante dinámica browniana, la membrana celular, los ribosomas y el transportador transmembrana de azúcares PtsG, y la simulación preliminar del reparto de cromosomas impulsado únicamente por la acción de las proteínas SMC. El cromosoma materno aparece en verde y los cromosomas hijos, en rosa y azul. Cortesía: Cell / DOI: 10.1016/j.cell.2026.02.009
La vida microscópica, al detalle
El modelo permite examinar fenómenos que serían muy difíciles de observar directamente en un experimento. Por ejemplo, los investigadores pudieron seguir cuántos ribosomas —las fábricas de proteínas— están activos en cada momento. Según la simulación, alrededor del 55 % de los ribosomas están traduciendo proteínas simultáneamente, mientras que cerca del 70 % de las enzimas ARN polimerasas están transcribiendo genes.
También permite medir la vida media del ARN mensajero —la molécula que transporta la información genética del ADN hasta los ribosomas, donde se utiliza como instrucción para fabricar proteínas—, que en la simulación varía desde menos de un minuto hasta unos veinte minutos, un rango similar al observado en otras bacterias.
Otro aspecto interesante es cómo se reparten las moléculas entre las dos células hijas. Como ocurre en organismos reales, el reparto es en gran medida aleatorio: algunas proteínas quedan ligeramente más concentradas en una célula que en la otra. Ese tipo de variabilidad puede influir en el comportamiento posterior de cada célula.
Un superordenador para cada célula
La precisión del modelo tiene un coste enorme. Simular un único ciclo celular completo requiere entre cuatro y seis días de cálculo en dos potentes unidades de procesamiento gráfico (GPU), el tipo de procesador utilizado para la inteligencia artificial (IA).
En total, los investigadores ejecutaron medio centenar de simulaciones independientes, lo que supuso unas 15.000 horas de computación.
🗣️ «No puedo exagerar lo difícil que es simular cosas que se mueven, y hacerlo en 3D para una célula completa fue... triunfal —recuerda Thornburg—. Uno de los últimos grandes obstáculos que Andrew y yo tuvimos que resolver fue comprender cómo la membrana y el ADN se comunican entre sí cuando ambos se mueven».
Este requisito limita todavía el número de células que se pueden estudiar, pero los autores creen que los avances en hardware y algoritmos permitirán ampliar estas simulaciones en el futuro.
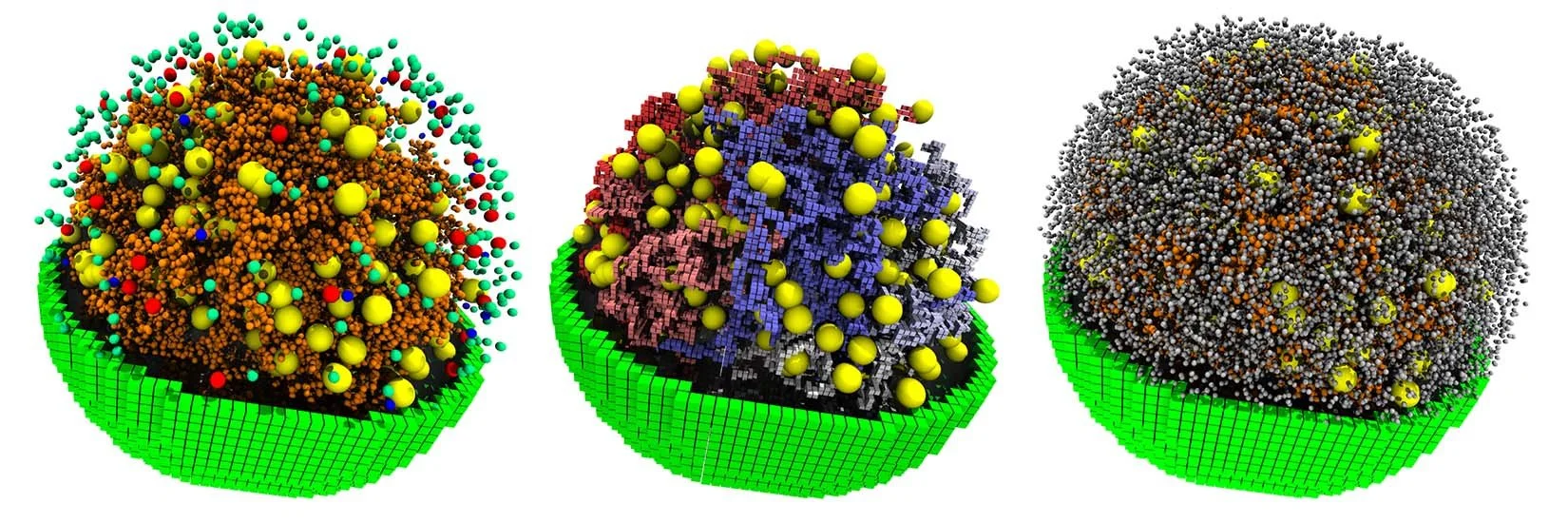
Simulación de una célula en las primeras etapas de la división de JCVI-syn3A. La mitad izquierda muestra la membrana (cubos verdes) y los ribosomas (amarillo/púrpura) entrelazados con el cromosoma celular (rojo). La mitad derecha muestra todas las proteínas (gris) y el ARN (naranja) dentro de la célula, con un pequeño corte que revela una segunda copia del cromosoma (azul). Cortesía: Zane Thornburg
El sueño de la célula virtual
El objetivo a largo plazo de este tipo de investigaciones es crear modelos completos de células que permitan realizar experimentos digitales. En lugar de modificar genes en el laboratorio y esperar a ver qué ocurre, los científicos podrían probar primero sus hipótesis en un ordenador.
Un modelo así permitiría, por ejemplo:
✅ Predecir cómo afectará una mutación genética al funcionamiento de una célula.
✅ Diseñar organismos sintéticos.
✅ Comprender mejor los mecanismos fundamentales de la vida.
Los autores consideran que su simulación constituye una base para avanzar hacia ese objetivo. La célula mínima Syn3A ofrece «una plataforma con los componentes esenciales de la vida», sobre la que se pueden añadir progresivamente nuevos procesos biológicos.
«Tenemos un modelo de célula completa que predice muchas propiedades celulares al mismo tiempo —explica Luthey-Schulten. Y añade—: Si quieres saber qué está pasando, por ejemplo, en el metabolismo de los nucleótidos, también puedes ver qué ocurre en la replicación del ADN y en la biogénesis de los ribosomas. Así que las simulaciones pueden darte los resultados de cientos de experimentos simultáneamente.”
Lo que aún falta por entender
Aun así, el modelo dista de ser perfecto. Algunas funciones celulares todavía no están representadas con todo detalle. Por ejemplo, el modelo no incluye completamente procesos como la transcripción genética en operones —grupos de genes que se expresan juntos— ni el comportamiento cooperativo de los ribosomas en la traducción de proteínas.
También quedan incógnitas sobre cómo se separan físicamente los cromosomas en la división celular o cómo influyen ciertos procesos metabólicos en la dinámica genética.
Para mejorar el modelo, los investigadores subrayan la necesidad de nuevos datos experimentales, desde mediciones completas del metabolismo celular hasta estudios globales de la estabilidad del ARN o la vida media de las proteínas.
El equipo de investigación incluye, de izquierda a derecha, al profesor de Química Angad Mehta, al estudiante de posgrado Enguang Fu, al investigador posdoctoral Zane Thornburg, a la profesora de Química Zan Luthey-Schulten y al estudiante de posgrado Andrew Maytin. Cortesía: Michelle Hassel.
Comprender las reglas de la vida
A pesar de sus limitaciones, la simulación marca un hito en la biología computacional. Durante décadas, los científicos han aspirado a comprender cómo miles de procesos químicos y físicos se coordinan para producir algo tan aparentemente simple como una célula que crece y se divide.
La nueva célula virtual no responde todavía a todas las preguntas, pero ofrece algo inédito: un laboratorio digital donde observar la vida en funcionamiento, molécula a molécula.
Si los modelos continúan mejorando, es posible que en el futuro los biólogos puedan explorar organismos completos dentro de un ordenador. Y entonces, quizá por primera vez, podremos experimentar con la vida sin necesidad de tocarla.▪️(9-marzo-2026)
Información facilitada por la Universidad de Illinois en Urbana-Champaign
Fuente: Thornburg, Zane R. et al. Bringing the genetically minimal cell to life on a computer in 4D. Cell (2026). DOI: 10.1016/j.cell.2026.02.009